|
基因表达连续性分析
一、简介
基因表达连续性分析(serial analysis of gene expression,SAGE )是1995年由美国霍普金斯大学医学院Velculescu等发明的一种新的基因表达转录组分析技术。
二、原理
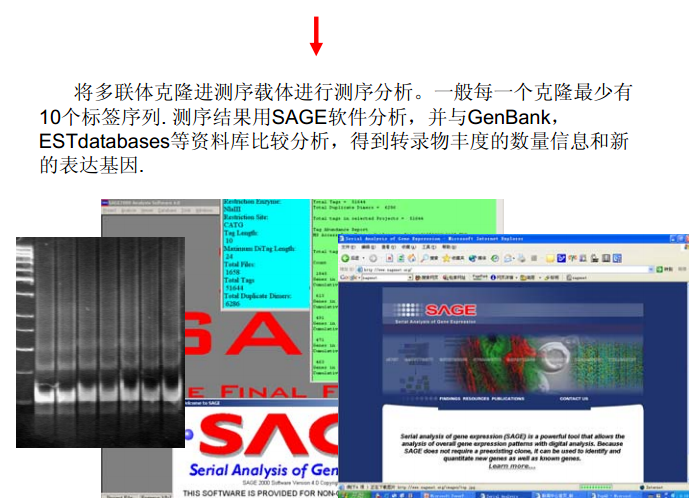
来自于任一转录本特定区域的长度仅10~14bp的短核苷酸序列,就已包含了足够的信息以特异性地确定该转录本。例如:一个10碱基的序列能有410=1048576种不同的排列组合,而人类基因组据估计仅编码80000种转录本,因此在理论上每一个10碱基标签就能够代表一种转录本的特征序列。将短片段两两随机配对,形成双标签体 (Ditag),在标签的种类、数量极大丰富的情况下,完全相同的双标签体出现的概率趋近于零。将这些双标签体相互连接、集中形成长的DNA分子,对其进行测序将能得到大量连续的单个标签,并能以连续的数据形式进行处理。这样就可对数以千计的mRNA 转录本进行批量分析。各转录本的表达水平也就可以用特定标签被测得的次数来进行精确定量了。
三、实验流程
.png)
.png)
.png)
四、特点
1. 较全面获取生物的基因表达信息;
2. 对基因序列没有选择性;
3. 所需的样品量极少 (100 ngmRNA);
4. 具有较好的重复性;
5. 同表达谱芯片技术具有互补性;
6. 成本较高,需测序,方法较复杂;
7. 10 bp 序列表征基因尚有缺陷。
|